Team:Chiba/Project/j
From 2008.igem.org
| ホーム | メンバー紹介 | プロジェクト紹介 | 作成したDNAパーツ | ノート |
|---|
より詳しいプロジェクト内容はこちらのページに英語で記載されています。
Contents |
プロジェクトデザイン
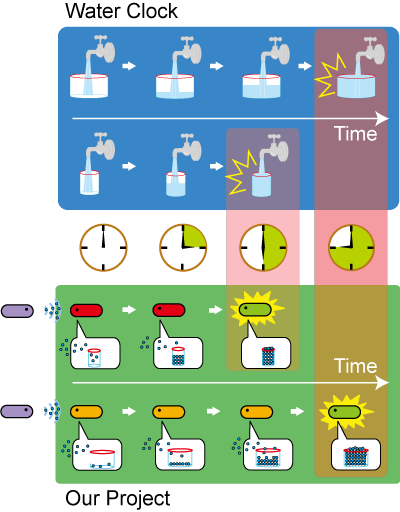
[http://en.wikipedia.org/wiki/Water_clock Water clock-wikipedia.en 水時計]のような働きをする大腸菌をデザインした。Fig.3にその機構を示す。
1. センダーは、シグナル分子をゆっくりと一定の速度で合成する。シグナル分子は代謝されない(あるいは現実的な時間スケールであれば事実上代謝されない)ために、ゆっくりと時間をかけて(線形に)蓄積される。
2. レシーバーはシグナル分子の濃度が閾値に達したときに初めて、シグナル分子を感知し遺伝子スイッチをオンにする。異なるシグナル分子の場合、遺伝子スイッチは異なる速度で活性化される。システム全体は順番を持って起動するスイッチとして働く。
3.レシーバーの感度を変える、またはシグナル分子の蓄積速度を変えることで、スイッチの遅延時間を変えることができる。いくつかの遅延時間を持ったスイッチを使うことで、異なる多数の細胞機能を、順番に活性化することができる.
シグナリングシステム
本プロジェクトでは、シグナル分子としてアシルホモセリンラクトン(AHL)使用する。センダーは、LuxIあるいは類似の酵素を常時発現する。これら酵素はAHLsの合成を触媒する。すべての細胞はおおよそ一定の速度でAHLを合成する。AHLは細胞膜を透過し、近傍の細胞に感知される。レシーバーはLuxRタンパク質あるいは類似のタンパク質を常時発現する。AHLはLuxRタンパク質と結合し、AHL-LuxR複合体を形成する。この複合体は、Luxプロモーターを活性化する。LuxプロモーターがONになるAHL濃度は、AHLと個々のLuxRタンパク質との親和性により決定される。(3),(4). (more about quorum sensing)
Controlling the Delay time of the AHL signaling
LuxIのつくるAHLに対して、感度差による応答時間差は、2つの方法で実現することができる。
- LuxR/ Pluxの感度変異体を用いる
LuxRの変異体を用いれば、pluxがonになるAHL濃度が<1nMから~10nMまで変化する。[http://authors.library.caltech.edu/5553/ C. H. Collins.et al.Mol.Microbiol.2005.55(3).712–723] - クロストークを使う(その1)
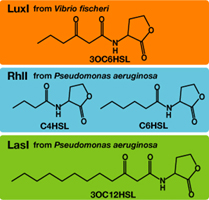
AHL=Acyl-homoserine Lactoneには、そのアシル基が異なる種類がある。luxIが合成するAHLは、3-oxo-hyxanoyl-Homoserine Lactone (=OHHL)であり、3-oxo-dodecanoyl-homoserine Lactone(=ODHL)や、butyryl-homoserine Lactone(=HHL)が存在する。それぞれ、合成酵素はLasI、RhlI(ともにシュードモナス由来)と呼ばれる。このほかのAHL分子と、その合成酵素を以下に示した。これらのAHL分子は、アシル基のみが異なるため、一定の割合でLuxRと相互作用する(cross-talkする)。たとえば、OdHLとLuxRとのcross-talk(LasI-LuxR)は、OHHLとLuxRの場合(LuxI-LuxR)の1/100である.[http://www3.interscience.wiley.com/journal/119124142/abstract M.K Winson et al.:FEMS Microbiology Letters(1998)]
AHL分子の蓄積速度が一定ならば,luxI-LuxR/Pluxよりも20倍遅くスイッチが入ることとなる。
- クロストーク(その2)-LuxR/ Pluxの感度変異体を用いる場合-
LuxRの変異体(LuxR-G2E,LuxR-G2E-R67M)を用いると、3OC6HSL以外のAHLs(C10HSL, C6HSL, C8HSL, C12HSL,3OC12HSL)に対しても、receiverが活性化される。[http://www.nature.com/nbt/journal/v24/n6/abs/nbt1209.html C. H. Collins. et al.Nature Biotechnology.24, 708 - 712 (2006)]
Construction(From BioBrick)
More about Quorum Sensing
- [http://parts.mit.edu/registry/index.php/Featured_Parts:Cell-Cell-Signaling Cell-Cell-Signaling]
- [http://www.che.caltech.edu/groups/fha/quorum.html About Quorum sensing]
How Our System Works
| ホーム | メンバー紹介 | プロジェクト紹介 | 作成したDNAパーツ | ノート |
|---|
 "
"